Clear Sky Science · de
cfGWAS enthüllen die genetische Grundlage von Endmotiven in zellfreier DNA
DNA-Spuren, die in unserem Blut treiben
Unablässig schweben winzige DNA-Fragmente durch unser Blut, freigesetzt von sterbenden und sich erneuernden Zellen. Ärztinnen und Ärzte nutzen diese „zellfreie DNA“ bereits zur Schwangerschaftsdiagnostik und zur Suche nach frühen Krebsanzeichen, doch wir wissen noch wenig darüber, wie diese Fragmente entstehen und wieder verschwinden. Diese Studie nutzt genetische Spurensuche in bislang ungekanntem Umfang, um aufzudecken, welche menschlichen Gene die feinen Muster an den Enden dieser DNA-Fragmente formen — Informationen, die Liquid-Biopsien präzisieren und auf neue Behandlungsansätze für immunologische und entzündliche Erkrankungen hinweisen könnten. 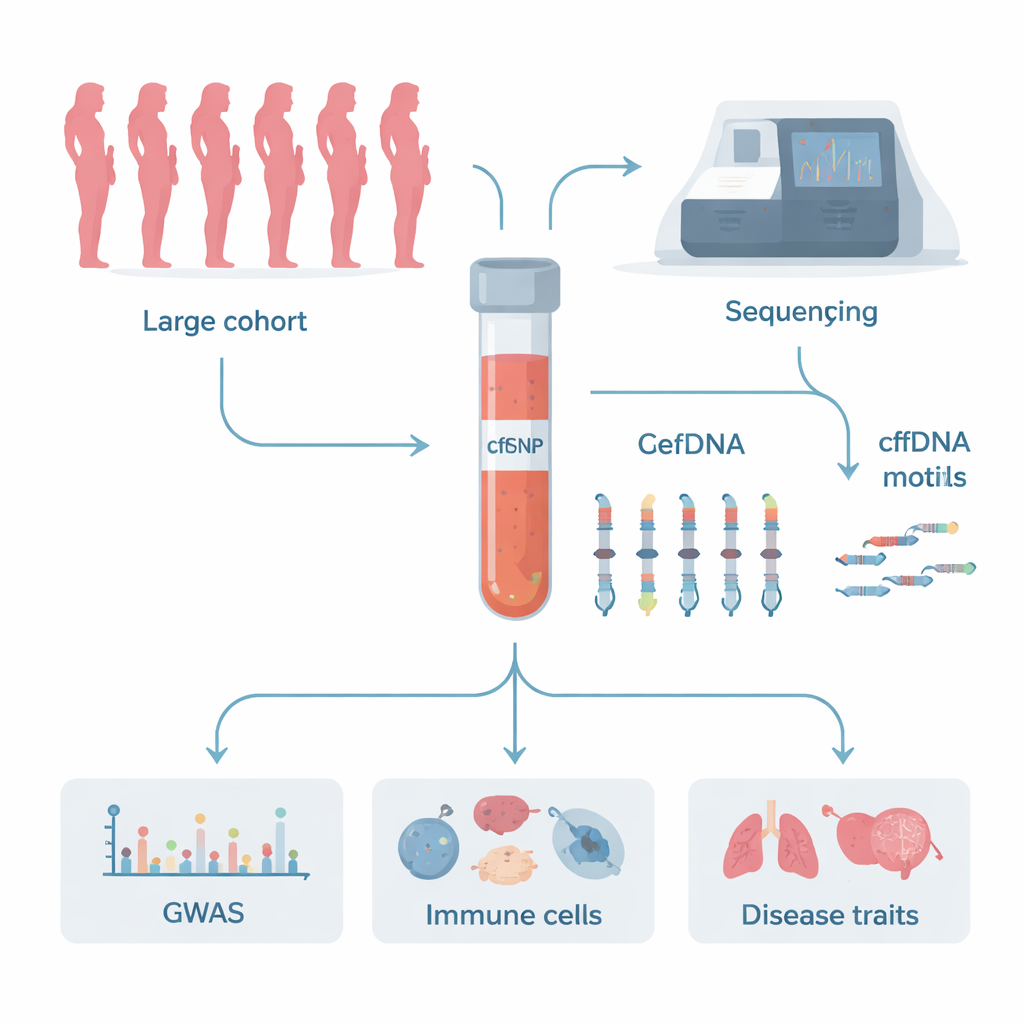
Was sind diese frei schwebenden DNA-Fragmente?
Zellfreie DNA (cfDNA) besteht aus kurzen Stücken genetischen Materials, die beim Zelltod oder durch aktive Freisetzung in Körperflüssigkeiten wie Blut, Speichel und Urin gelangen. Während einer Schwangerschaft ermöglicht die fetale cfDNA im Blut der Mutter nichtinvasive Pränataltests. Bei Krebs kann tumorabgeleitete cfDNA die Krankheit melden, lange bevor ein Tumor sichtbar ist. Über die bloße Menge an cfDNA hinaus richten Forschende jetzt ihr Augenmerk auf die „Fragmentomik“: wie lang die Stücke sind, wie sie geschnitten wurden und welche kurzen Buchstabenmuster, sogenannte „Endmotive“, an den Anfangsenden der Fragmente auftreten. Diese Endmotive wirken wie molekulare Fingerabdrücke dafür, wie und wo DNA zerteilt wurde, und spiegeln die Aktivität von Enzymen sowie die Arten der Zellen wider, die die DNA beigetragen haben.
Ein gigantischer genetischer Scan von DNA-Fragmentmustern
Um herauszufinden, welche Gene diese Endmotive beeinflussen, führten die Autorinnen und Autoren eine neue Form der genomweiten Assoziationsstudie durch, die sie cfGWAS nennen. Sie analysierten Blutproben von 28.016 schwangeren Frauen in China, die sich routinemäßigen pränatalen Untersuchungen unterzogen. Aus denselben Low-Coverage-Sequenzierungsdaten gewannen sie sowohl die genetischen Varianten der Frauen als auch die detaillierten Frequenzen aller 256 möglichen vierbuchstabigen Endmotive an den Spitzen der cfDNA-Fragmente. Mithilfe statistischer Modelle, die Alter, Schwangerschaftswoche und technische Faktoren berücksichtigten, durchsuchten sie fast 2,9 Millionen häufige genetische Varianten, um zu sehen, welche mit Veränderungen dieser Motivmuster zwischen Individuen korrelierten.
Wichtige Gene dahinter, wie DNA zerschnitten wird
Die cfGWAS identifizierte 15 besonders robuste genetische Regionen, die mit 176 verschiedenen Endmotiven verknüpft sind. Einige Treffer bestätigten die Schlüsselrolle bekannter DNA-schneidender Enzyme, darunter DFFB und DNASE1L3, die bei programmierter Zellteilung DNA zerkleinern, sowie ein verwandtes Enzymgen, DNASE1L1. Überraschender war das stärkste Signal, das von PANX1 ausging — einem Gen, das einen Kanal in der Zellmembran kodiert und an Zellkommunikation, Entzündung und Zelltod beteiligt ist. Menschen mit unterschiedlichen Varianten dieser Gene zeigten unterschiedliche Muster, welche Endmotive in ihrem Blut häufig oder selten waren. Die Forschenden replizierten die meisten dieser Signale in drei unabhängigen Kohorten — darunter eine weitere große Schwangerschaftsgruppe in China, eine niederländische Schwangerschaftsstudie und eine kleinere Gruppe gesunder nicht-schwangeren Erwachsener — was zeigt, dass die Befunde robust sind und sich nicht auf ein einziges Krankenhaus oder Land beschränken. 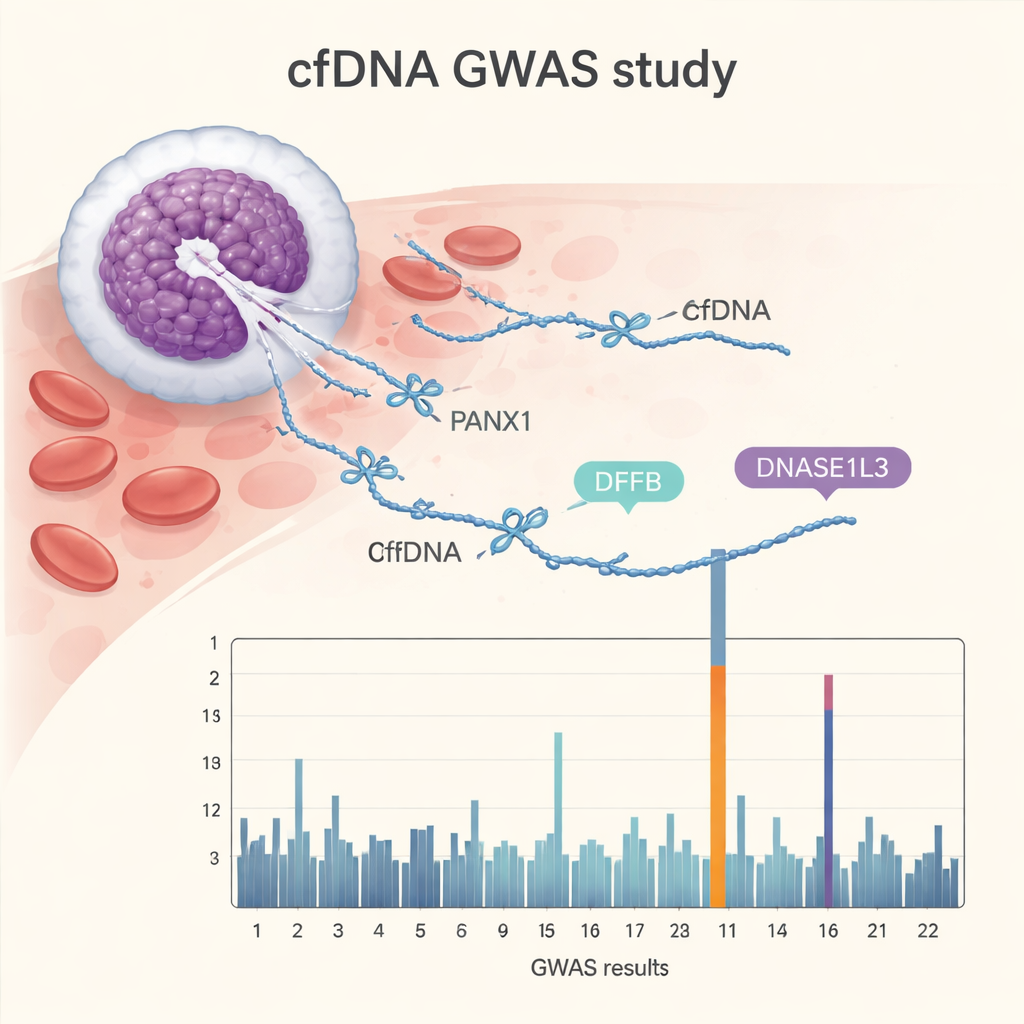
Von Genen zu Immunzellen und Körpermerkmalen
Genetische Signale wirken selten isoliert, daher untersuchten die Forschenden, wie cfDNA-Motive mit anderen in denselben schwangeren Frauen gemessenen Merkmalen zusammenhängen. Durch den Vergleich ihrer cfDNA-Ergebnisse mit genomweiten Scans von 104 klinischen Messwerten — etwa Blutbild, Körpergewicht und Leberfunktion — fanden sie gemeinsame genetische Grundlagen zwischen bestimmten Endmotiven und Merkmalen wie Body-Mass-Index, weißen Blutkörperchen und insbesondere Neutrophilen. Detailliertere kausale Analysen deuteten darauf hin, dass Veränderungen in Immunzellen, eher als die cfDNA selbst, die Verschiebungen in den Motivmustern antreiben. Zusätzliche Pfad- und Gewebeanalysen wiesen auf eine zentrale Rolle von Blut- und Immunzellen hin — insbesondere Neutrophilen, die während Immunreaktionen DNA-Netzwerke ausstoßen können — bei der Produktion und Beseitigung von cfDNA. Experimentelle Arbeiten an Mäusen und in Zellkulturen, in denen PANX1 ausgeschaltet wurde, bestätigten, dass dieses Gen direkt sowohl die Vielfalt der Endmotive als auch die Gesamtmenge an freigesetzter cfDNA verändert.
Warum das für die Medizin von morgen wichtig ist
Für Nicht-Spezialisten mag die Idee, vierbuchstabige Muster an den Enden von DNA-Fragmenten zu verfolgen, esoterisch klingen. Doch diese Arbeit zeigt, dass diese Muster kein zufälliges Rauschen sind: Sie sind erblich, werden von bestimmten Genen geprägt, stehen in engem Zusammenhang mit dem Verhalten von Immunzellen und reagieren auf Körpermerkmale wie Gewicht. Da weltweit bereits Millionen von Menschen cfDNA-Sequenzierungen für pränatale Screenings und Krebsuntersuchungen erhalten haben, könnten dieselben Daten mithilfe von cfGWAS erneut analysiert werden, um weitere Gene zu entdecken, die die DNA-Fragmentierung und -Elimination steuern. Langfristig könnte dieses Wissen Liquid-Biopsie-Tests verfeinern, helfen zu unterscheiden, welche Gewebe abnorme DNA freisetzen, und sogar auf Medikamentenziele hinweisen, um entweder die DNA-Beseitigung zu fördern — etwa bei Autoimmunerkrankungen — oder fragile Tumor-DNA zu erhalten, um die Früherkennung zu verbessern.
Zitation: Zhu, H., Zhang, Y., Li, L. et al. cfGWAS reveal genetic basis of cell-free DNA end motifs. Nat Commun 17, 1714 (2026). https://doi.org/10.1038/s41467-025-67940-w
Schlüsselwörter: zellfreie DNA, genomweite Assoziationsstudie, Liquid Biopsy, Immunzellen, Schwangerschaft