Clear Sky Science · de
Ein langer Weg zu verlässlichen und vollständigen Genomen von Heilpflanzen
Warum Landkarten der Pflanzen‑DNA für die menschliche Gesundheit wichtig sind
Viele der heute wirksamsten Arzneimittel – von Krebsmedikamenten wie Paclitaxel bis zu Schmerzmitteln wie Morphin und dem Antimalariamittel Artemisinin – stammen aus Pflanzen. Für die meisten Heilpflanzen fehlt Forschenden jedoch noch ein vollständiges „Handbuch“ ihrer DNA. Diese Übersicht erläutert, wie neue Genomtechnologien unsere Fähigkeit verbessern, diese Handbücher zu lesen, warum aktuelle Pflanzengenome oft unvollständig oder fehlerhaft sind und wie wirklich genaue Genome bessere Medikamente, nachhaltigere Produktionswege und verbesserten Schutz wertvoller Arten ermöglichen könnten.
Das Versprechen, die Baupläne von Heilpflanzen zu entschlüsseln
Seit Jahrtausenden verlassen sich Menschen auf pflanzliche Heilmittel, und die moderne Pharmakologie schöpft weiterhin stark aus natürlichen Pflanzenprodukten. Diese spezialisierten Moleküle – Alkaloide, Terpenoide, phenolische Verbindungen und viele andere – entstehen über komplexe Stoffwechselwege, die in der Pflanzen‑DNA verschlüsselt sind. Bis vor kurzem mussten Forschende diese Wege mit langsamen, arbeitsintensiven Methoden wie Isotopenverfolgung und dem Klonieren einzelner Gene zusammenpuzzeln. Die Verfügbarkeit erschwinglicher, hochdurchsatzfähiger DNA‑Sequenzierung hat das Feld verändert. Bis Februar 2025 waren Genome von 431 heilpflanzenbezogenen Proben (aus 203 Arten) sequenziert, was Forschenden systematische Möglichkeiten bietet, nach Wegesgenen zu suchen, zu verstehen, wie wertvolle Verbindungen reguliert werden, und zu untersuchen, wie diese Chemien evolviert sind.
Ein Boom bei Sequenzierungen, aber viele unvollkommene Genome
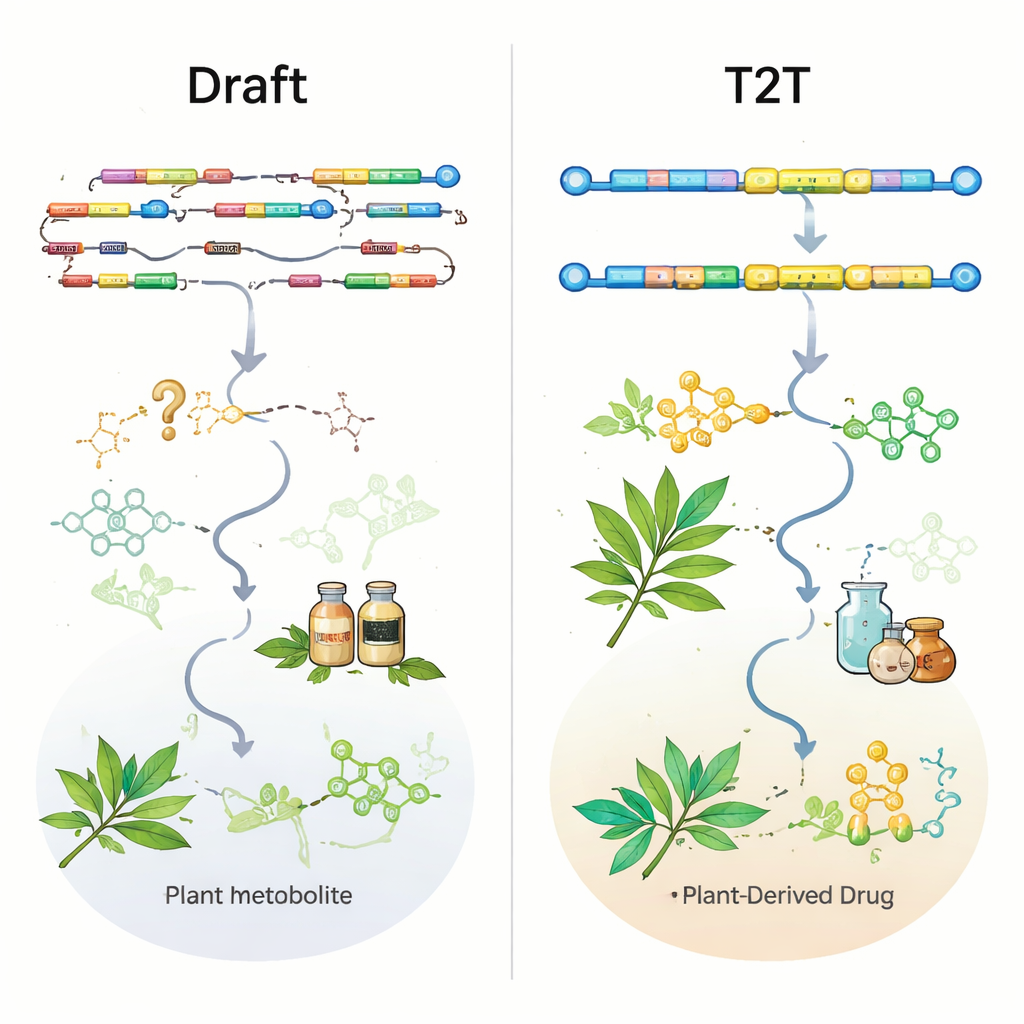
Langread‑Sequenzierungstechnologien von PacBio und Oxford Nanopore, kombiniert mit Short‑Read‑Illumina‑Daten und chromosomalen Kartiermethoden wie Hi‑C, haben die Qualität von Pflanzengenenom deutlich verbessert. Fast die Hälfte aller Assemblies von Heilpflanzen wurde erst in den letzten drei Jahren veröffentlicht, und die meisten neueren Genome sind nun auf Chromosomenebene aufgebaut. Die Übersicht zeigt jedoch, dass die Menge die Qualität überholt hat. Mehr als die Hälfte der Genome existiert nur in einer ersten Version, viele bleiben auf Draft‑Niveau, und lediglich 11 Heilpflanzen besitzen „Telomer‑bis‑Telomer“ (T2T) lückenlose Assemblies, die Centromere und andere repetitive Regionen vollständig erfassen. Standardmetriken wie N50 (ein Maß für Kontiguität) und BUSCO‑Werte (ein Maß für konservierte Gene) wirken insgesamt ermutigend, können aber kritische Lücken verschleiern – gerade dort, wo Schlüsselgene der Biosynthese liegen.
Verborgene Lücken genau dort, wo die Wirkstoffgene sein sollten
Um zu prüfen, wie nützlich aktuelle Genome wirklich sind, untersuchten die Autorinnen und Autoren bekannte, experimentell validierte Wegesgene in neun gut untersuchten Heilpflanzen. Selbst in einigen Assemblies auf Chromosomenebene fehlten wichtige Enzyme für Verbindungen wie Ginsenoside in Ginseng oder Artemisinin in Artemisia annua vollständig oder waren nur teilweise abgebildet. In anderen Fällen waren Gene in der rohen Genomsequenz vorhanden, aber in den offiziellen Genannotationen fehlten sie oder waren verkürzt, sodass sie schwer zu finden waren. Ein auffälliges Beispiel liefert das kumarinbildende Kraut Peucedanum praeruptorum: Ein älteres Chromosomenlevel‑Genom zerstückelte ein Schlüssengen und verpasste zwei weitere; eine neuere T2T‑Assembly stellte diese Gene nicht nur wieder her, sondern zeigte auch, dass mehrere von ihnen gemeinsam in einem eng gepackten biosynthetischen Gencluster sitzen. Solche Clusterkarten sind genau das, was Forschende brauchen, um Pflanzen oder Mikroben so zu konstruieren, dass sie Arzneistoffe effizienter produzieren.
Warum Pflanzengeneome so schwer zu assemblieren sind
Heilpflanzen stellen besondere Herausforderungen dar, die über jene vieler Kulturpflanzen hinausgehen. Ihre Genome weisen oft hohe Heterozygosität (viele DNA‑Unterschiede zwischen den beiden Chromosomenkopien), häufige Polyploidie (mehrere Chromosomensätze) und große Anteile repetitiver DNA auf – Merkmale, die Assemblierungsalgorithmen verwirren und zu Brüchen oder Fehlverknüpfungen führen. Etwa ein Drittel der sequenzierten Heilpflanzen hat einen repetitiven Anteil von mehr als 70 %, und bei über einem Viertel wurde sehr hohe Heterozygosität festgestellt. Das Aufbauen stark eingezüchteter Linien oder das Isolieren haploider Gewebe kann helfen, ist aber für viele Arten langsam, teuer oder biologisch schwierig. Neue Strategien, die jede elterliche Haplotypasseparat assemblieren, und leistungsfähigere Algorithmen, die auf repeat‑reiche, polyploide Genome abgestimmt sind, beginnen, diese Hürden zu mindern, sind aber noch nicht Routine.
Von Genomen zu neuen Arzneimitteln und künftigen Richtungen
Sind Genome ausreichend gut, werden sie zu mächtigen Treibern von Entdeckungen. Forschende können vollständige Genomdaten mit Transkriptomik, Metabolomik und synthetischer Biologie kombinieren, um Enzyme, regulatorische Gene und biosynthetische Gencluster zu identifizieren, die die Produktion wertvoller Verbindungen steuern. Diese Erkenntnisse ermöglichten bereits die Rekonstruktion komplexer Pflanzenwege – etwa die für Vinblastin, Paclitaxel und viele andere Arzneistoffe – in Hefen oder Modellpflanzen und ebnen den Weg zu stabiler, großskaliger Bioproduktion. Die Autorinnen und Autoren plädieren künftig für einen Wandel von „einem groben Genom pro Art“ hin zu mehreren hochwertigen, T2T‑ und haplotypaufgelösten Assemblies, die die innerartliche Vielfalt erfassen, ähnlich Pan‑Genomen in der Kulturpflanzenforschung. Die Kopplung dieser Referenzgenome mit umfangreichen Resekquenzierungsprojekten, fortgeschrittener Phänotypisierung und aufkommenden Einzelzell‑ sowie raumbezogenen Transkriptomikmethoden sollte beleuchten, wie Umwelt, Zelltyp und Genetzwerke zusammenwirken, um die medizinische Chemie zu formen.
Was das für Patientinnen, Patienten und den Planeten bedeutet
Die zentrale Botschaft der Übersicht lautet, dass verlässliche, vollständige Genome von Heilpflanzen kein Luxus sind; sie sind die Grundlage dafür, jahrhundertelanges Kräuterwissen in präzise, moderne Therapien zu überführen. Bessere Genome helfen Forschenden, fehlende Schritte in Wirkstoffwegen zu finden, sicherere und reichlichere Vorräte kritischer Arzneimittel zu konstruieren und alternative Arten zu identifizieren, die dieselben Verbindungen produzieren können. Sie werden auch Naturschutz und nachhaltige Nutzung bedrohter Heilpflanzen leiten, von denen die meisten noch keine genomischen Ressourcen besitzen. Kurz gesagt: Das vollständige und genaue Kartieren dieser Genome könnte die Arzneimittelentdeckung beschleunigen, Lieferketten stabilisieren und die botanische Vielfalt bewahren – alles zum Wohl der menschlichen Gesundheit.
Zitation: Cheng, LT., Wang, ZL., Zhu, QH. et al. A long road ahead to reliable and complete medicinal plant genomes. Nat Commun 16, 2150 (2025). https://doi.org/10.1038/s41467-025-57448-8
Schlüsselwörter: Genomik von Heilpflanzen, biosynthetische Gencluster, Telomer‑bis‑Telomer‑Genome, Biosynthese natürlicher Produkte, Synthetische Biologie