Clear Sky Science · ar
تمكن DANST من فك تشابك أنواع الخلايا في النسخ المكانية باستخدام شبكات عصبية عدائية عميقة
رؤية الخلايا في حيّزها
الأنسجة البشرية هي مدن مكتظة بأنواع خلايا متعدّدة، لكل منها دوره الخاص. تقنيات «النسخ المكاني» الحديثة يمكنها قياس الجينات النشطة عبر شريحة نسيجية، لكن كل قياس غالبًا ما يمزج إشارات من عدة خلايا متجاورة. تقدم هذه الورقة طريقة حسابية ذكية اسمها DANST تفصل هذه المزيجات. عبر إخبارنا بأي أنواع الخلايا موجودة وأين توجد في الأعضاء والأورام، تساعد العلماء على فهم أفضل لكيفية بناء الأنسجة، وكيفية انتشار الأمراض، وأين قد تُوجّه العلاجات بشكل أمثل. 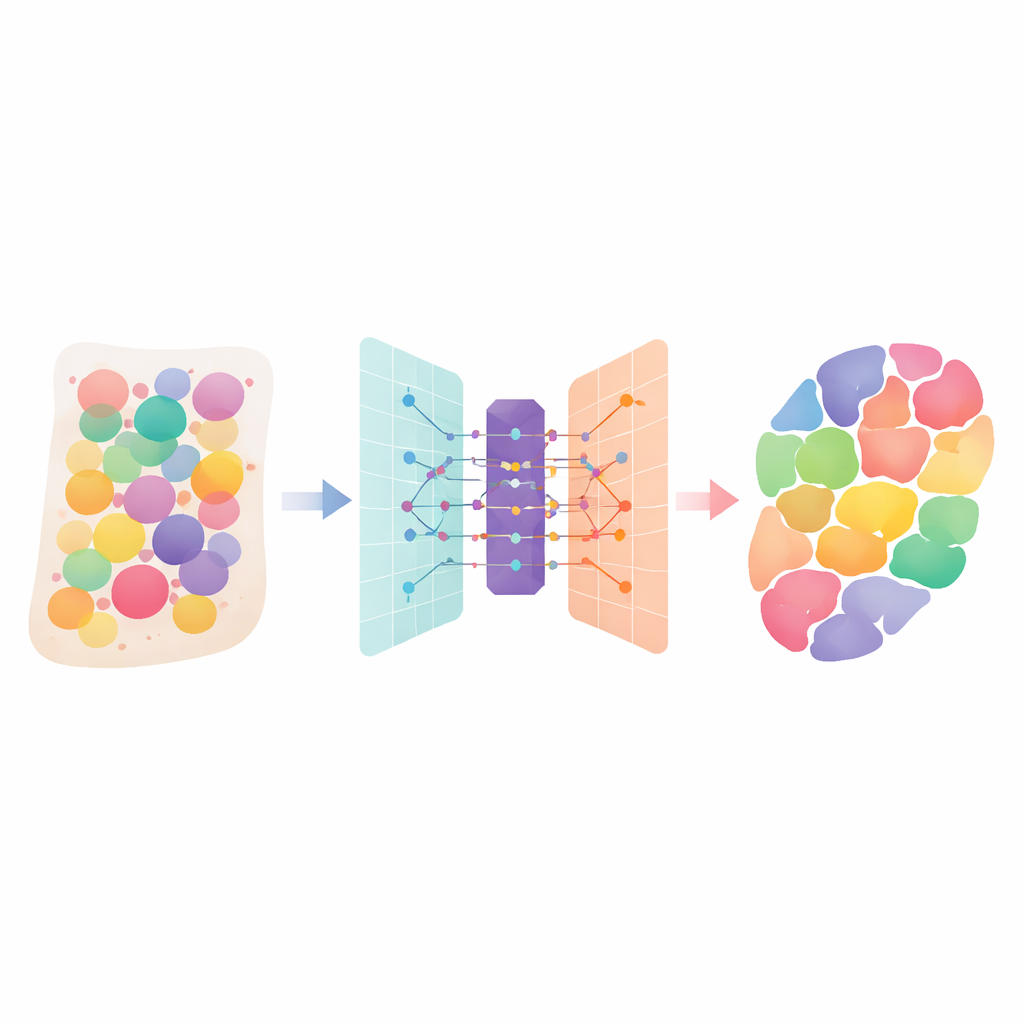
تحدّي تفكيك حشود الخلايا
يمكن لأدوات قراءة الجينات الحديثة إما أن تنظر بدقّة شديدة إلى الخلايا المفردة أو تلتقط التخطيط الكامل للنسيج، لكن نادرًا ما تجمع بين الدقّة والمشهد الشامل معًا. تسجّل تقنيات المكان الشائعة نشاط الجينات في «بقع» كبيرة نسبيًا قد تضم عدة خلايا. النتيجة تشبه سماع كورال دون معرفة من يغنّي أي نغمة. لفهم هذا، يحتاج الباحثون إلى طرائق «فك التشابك» التي تُقدّر مدى مساهمة كل نوع خلية في كل بقعة. العديد من الأساليب الحالية تستخدم بيانات الخلية المفردة كمرجع، لكنها تواجه صعوبة لأن نوعي البيانات تُجمَع بتجارب مختلفة ولا تتطابق تمامًا من حيث الجودة والضوضاء والدقّة.
بناء جسر بين عوالم البيانات
يتناول DANST هذا التباين بإنشاء جسر بين بيانات الخلايا المفردة والبيانات المكانية. أولًا، يستخدم ملفات الخلايا المفردة المفصّلة لمحاكاة العديد من البقع المختلطة الاصطناعية ذات نسب أنواع خلايا معروفة. في الوقت نفسه، يجمع البقع المكانية الحقيقية وفقًا لموقعها في النسيج وأنماط الجينات فيها، ويستخدم المسافات إلى هذه المجموعات ليُعيّن لكل بقعة مصطنعة «موقعًا زائفًا». تخلق هذه الخطوة خريطة مرتبطة حيث تتشارك البقع الاصطناعية والحقيقية إطارًا مكانيًا مشتركًا، مما يسمح للطريقة بتعلّم كيف تبدو الإشارات المختلطة في أحياء محددة من النسيج. 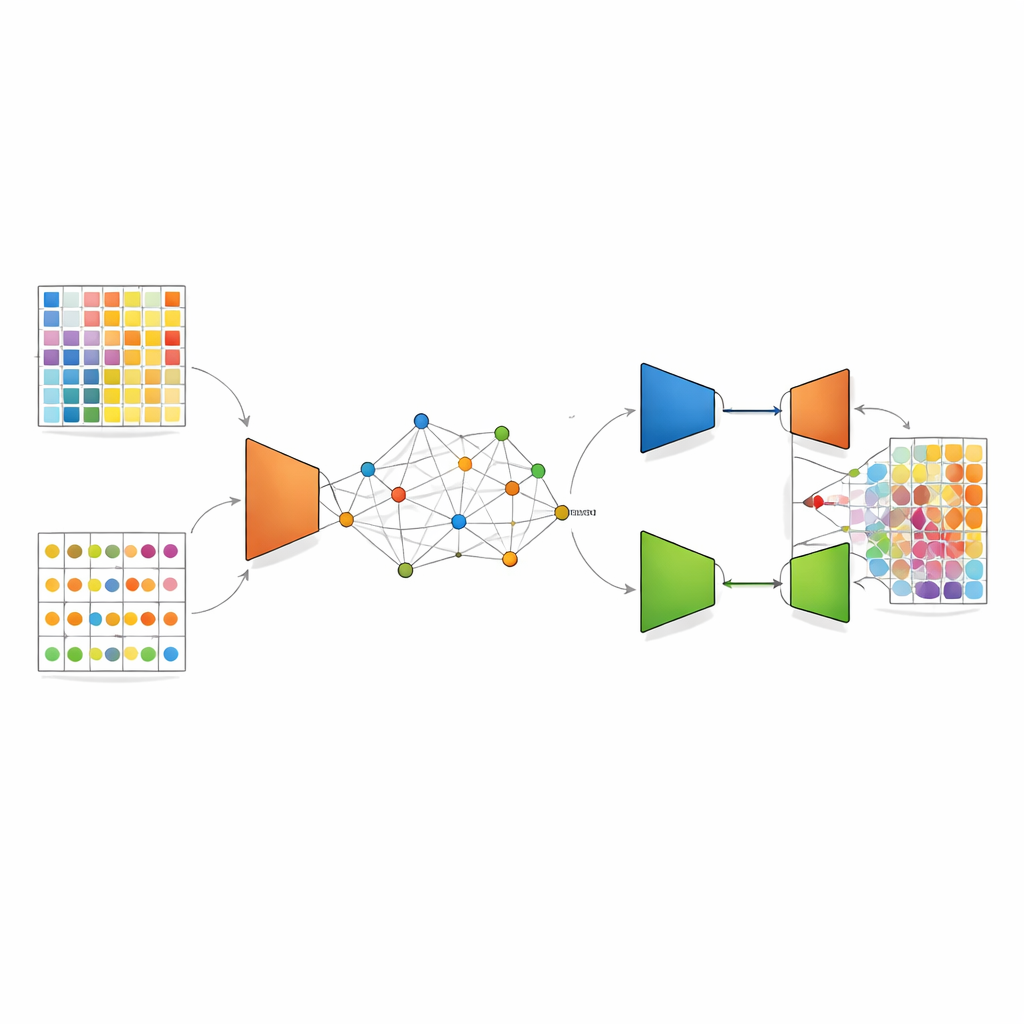
تنقية الإشارات ومحاذاة المجالات
حالما تُنشأ هذه الخريطة المشتركة، يطبّق DANST نوعًا من التعلّم العميق يُسمى المُشفر التبايني (variational autoencoder). تقوم هذه الشبكة بضغط أنماط الجينات من كل من البقع الحقيقية والمصطنعة إلى تمثيل داخلي مُنقّى ثم تحاول إعادة بنائها، محدثة بذلك تنقية للبيانات مع إبراز الميزات المهمة. فوق ذلك، يضيف المؤلفون مكوّنًا عدائيًا: شبكة ثانية تحاول أن تميّز ما إذا كان التمثيل المُنقّى مصدره بيانات مكانية حقيقية أم بيانات مُحاكاة، بينما يتعلّم مُستخلص الميزات أن يخدعها. هذا «صراع» يدفع النموذج نحو ميزات تعمل جيدًا لكلا مصدري البيانات، بحيث يمكن نقل المعرفة المستفادة من البقع المُحاكاة ذات نسب أنواع الخلايا المعروفة بصورة موثوقة إلى البقع النسيجية الحقيقية التي تُجهل تركيبتها.
الاختبار على قلوب وأدمغة وأورام
اختبر الفريق DANST على معايير اصطناعية وعينات بيولوجية حقيقية من الفئران والبشر. مقارنة بعدّة طرق رائدة، استعاد DANST نسب أنواع الخلايا في مجموعات بيانات صناعية بدقّة أعلى وحافظ على تفوّقه عبر أنسجة ومنصّات متباينة جدًا. في مجموعة بيانات لدماغ فأر، أعاد بوضوح التنظيم الطبقي للقشرة وتوافق مع مناطق تشريحية محددة من قبل الخبراء. في شريحة دماغ فأرية أخرى، التقط أنماطًا دقيقة في مناطق مثل الحُصين. والأهم من ذلك، في نسيج سرطان الثدي البشري، تتبّع DANST كيفية ترتيب خلايا مناعية مختلفة وخلايا داعمة وخلايا لمعية حسّاسة للهرمونات داخل مناطق الورم وحولها. توافقت هذه الخرائط مع المعرفة البيولوجية المعروفة واقترحت ميزات ذات صلة سريريًا، مثل الاعتماد الهرموني وإمكانية تنبؤ بتوقع أسوأ حيث كانت بعض الخلايا المناعية نادرة.
ماذا يعني هذا لعلم الأحياء والطب
بالنسبة لغير المتخصص،يمكن اعتبار DANST كمترجم قوي يحوّل الإشارات الضبابية والمتداخلة إلى صورة واضحة عن أي الخلايا تعيش أين في النسيج. من خلال فصل أنواع الخلايا في المكان بصورة موثوقة، يمنح الباحثين رؤية أوضح لكيفية تنظيم الأعضاء السليمة وكيف يعيد المرض تشكيل ذلك التنظيم. في السرطان، يمكن أن يكشف هذا كيف تتفاعل خلايا الورم والخلايا المناعية في مناطق محددة، ما قد يوجّه العلاجات المستهدفة ويساعد في التنبؤ بنتائج المرضى. ومع تزايد توفر مجموعات البيانات المكانية ومجموعات الخلايا المفردة، تُعد أدوات مثل DANST جاهزة لتصبح ضرورية لفك شفرة الأحياء الخلوية التي تقوم عليها الصحة والمرض.
الاستشهاد: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
الكلمات المفتاحية: النسخ المكانية, فك تشابك أنواع الخلايا, التعلّم العميق, البيئة الدقيقة للورم, تسلسل RNA خلية واحدة