Clear Sky Science · ar
إطار تعلم عميق قائم على DNABERT للتنبؤ بمواقع ارتباط عوامل النسخ
لماذا يهم التنبؤ بمفاتيح التحكم في الـDNA
تحمل كل خلية في جسمك تقريبًا نفس الـDNA، ومع ذلك تتصرف خلايا الدماغ والكبد والمناعة بشكل مختلف تمامًا. أحد الأسباب هو أن بروتينات خاصة تُسمى عوامل النسخ تعمل كمفاتيح جزيئية، تُشغّل أو تُطفئ الجينات عبر الارتباط بمقاطع قصيرة من الـDNA تُعرف بمواقع الارتباط. إيجاد جميع نقاط الارتباط تجريبيًا عبر الجينوم بطيء ومكلف. تقدم هذه الدراسة TFBS-Finder، نموذج ذكاء اصطناعي جديد يمكنه قراءة حروف الـDNA الخام والتنبؤ بدقة أكبر بمواقع ارتباط عوامل النسخ، مما قد يسرّع الأبحاث حول تنظيم الجينات والأمراض.
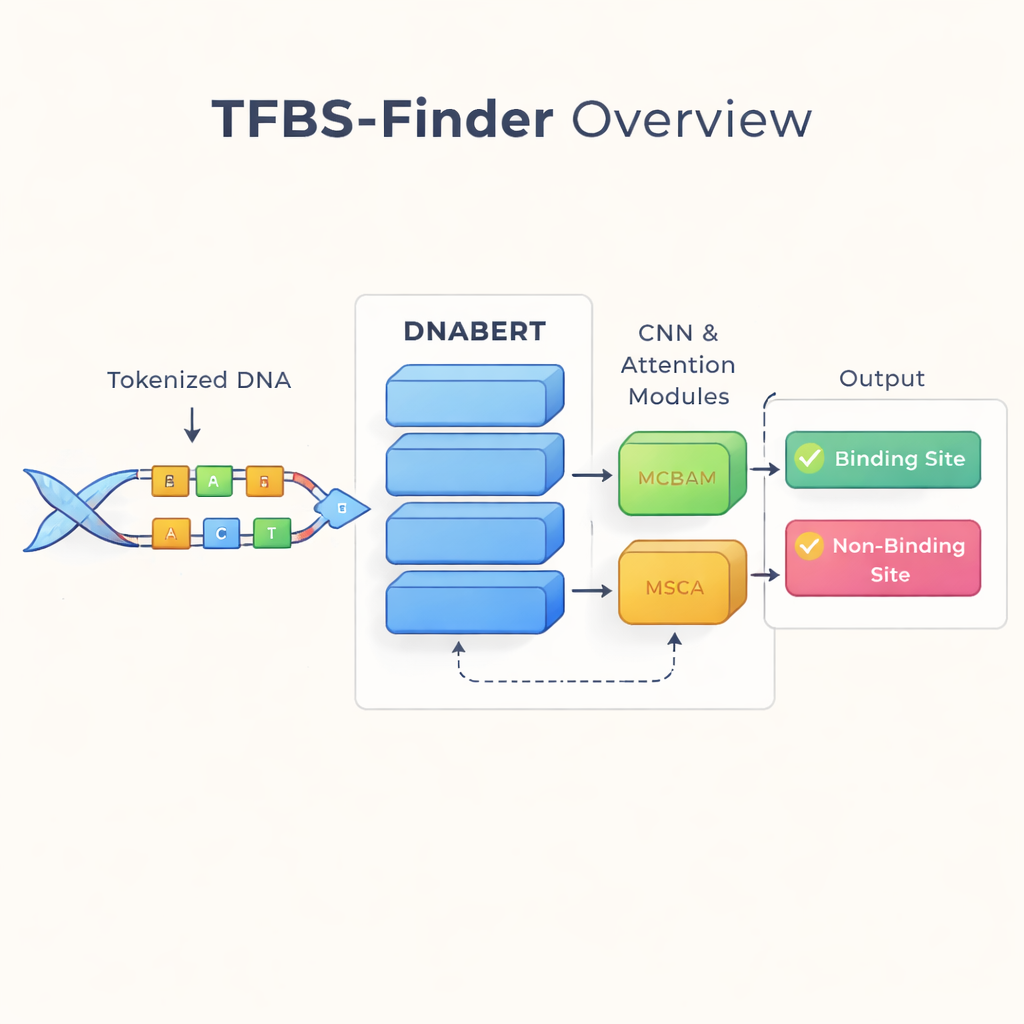
قراءة الـDNA كلغة
يبني المؤلفون على فكرة حوّلت تكنولوجيا اللغة: معاملة الـDNA كما لو كان نصًا. يستخدمون DNABERT، نسخة من نموذج اللغة BERT أعيد تدريبها على الـDNA البشري بدلًا من الكلمات. لا ينظر DNABERT إلى الحروف المفردة فحسب؛ بل يكسر الـDNA إلى «كلمات» متداخلة قصيرة مكونة من خمسة أحرف ويتعلم كيف تتكرر هذه الأجزاء معًا. هذا يمكّن النموذج من التقاط السياق على مدى بعيد، مثل كيفية ارتباط أنماط في طرف السلسلة بأنماط بعيدة، تمامًا كما نفهم معنى جملة بدلًا من كلمات منفردة.
اكتشاف الأنماط المحلية بانتباه مركز
بينما يجيد DNABERT التقاط السياق العام، يعتمد ارتباط عوامل النسخ غالبًا على دوافع قصيرة ودقيقة—أنماط محلية في الـDNA. لذلك يضيف TFBS-Finder عدة مكونات إضافية فوق DNABERT. شبكة عصبية التفافية (CNN) تمسح تمثيلات السلسلة لتبرز الأشكال المحلية المتكررة، على غرار كيف تكتشف برامج معالجة الصور الحواف والزوايا. ثم تعمل وحدتان انتباه، تُسمَّيان MCBAM وMSCA، ككشافات قابلة للضبط، تقوّي الميزات الأكثر إفادة وتخفف الضوضاء. معًا، توازن هذه الكتل بين رؤية الصورة الكبيرة والتفاصيل الدقيقة لتقرير ما إذا كانت قطعة الـDNA تحتوي موقع ارتباط حقيقي.
إثبات أن كل جزء مفيد حقًا
لاختبار ما إذا كانت كل هذه المكونات ضرورية، أجرى الفريق تجارب «الاستئصال» واسعة النطاق، حيث أزالوا أو أعادوا ترتيب الوحدات بشكل منهجي وأعادوا تدريب النظام على 165 مجموعة معيارية تغطي 29 عامل نسخ عبر 32 نوع خَلَوي. باستخدام مقاييس جودة التنبؤ القياسية، جاء نموذج TFBS-Finder الكامل في المقدمة باستمرار. النسخ الأبسط التي اعتمدت فقط على DNABERT، أو استبعدت إحدى وحدات الانتباه، فقدت الدقة بوضوح. وأكدت الاختبارات الإحصائية أن هذه الانخفاضات في الأداء لم تكن نتيجة صدفة، مما يدل على أن الجمع بين فهم التسلسل على مستوى شامل والانتباه المصمم بعناية للأنماط المحلية أمر حاسم.
العمل عبر أنواع الخلايا وتفوقه على الأدوات القديمة
سؤال مهم هو ما إذا كان نموذج مدرّب في سياق بيولوجي واحد يمكنه التعميم إلى سياق آخر. ركز المؤلفون على عامل نسخ مدروس جيدًا يُدعى CTCF ودربوا TFBS-Finder على بيانات من خط خلوي واحد، ثم اختبروه على خطوط أخرى. في كل التركيبات، حقق النموذج درجات عالية، مما يشير إلى أنه يلتقط ميزات جوهرية لارتباط CTCF المشتركة عبر الأنسجة. عند مقارنته بتسع طرق رائدة، بما في ذلك نماذج تعلم عميق ومرتكزة على BERT سابقة، أظهر TFBS-Finder دقة متوسطة أعلى وأنتج ترتيبًا أكثر موثوقية لمواقع الارتباط. كما عمل بسرعة أكبر قليلًا واستخدم ذاكرة أقل من أقرب نموذج سابق، مما يشير إلى أن الأداء الأفضل لم يتطلب حوسبة أثقل.
ماذا تعلم النموذج
تُنتقد أنظمة الذكاء المعقدة كثيرًا بأنها «صناديق سوداء». هنا، حاول الباحثون فتح تلك الصندوق عبر تصور مواقع الـDNA التي أثّرت أكثر على قرارات TFBS-Finder. لعاملَي نسخ لهما دوافع ارتباط معروفة جيدًا، CEBPB وGATA3، ولّدوا درجات أهمية على طول السلسلة وجمّعوا الإشارات الأقوى إلى أنماط توافقية. هذه الدوافع المستخرجة طابقت عن كثب الدوافع المرجعية من قواعد بيانات معتمدة، وتداخلت المناطق المتوقعة للارتباط مع حالات الدوافع المكتشفة بشكل مستقل. هذا يوحي بأن TFBS-Finder لا يكتفي بحفظ أمثلة بل تعلّم قواعد بيولوجية ذات معنى حول كيفية تعرف عوامل النسخ على الـDNA.
ماذا يعني هذا لعلم الوراثة والطب
يقدّم TFBS-Finder طريقة أكثر دقة وقابلة للتفسير لرسم خريطة مفاتيح التحكم المدمجة في حمضنا النووي. من خلال تحديد أماكن احتمال ارتباط عوامل النسخ، يمكن أن يساعد الباحثين في رسم شبكات تنظيم الجينات، وتحديد أي المتغيرات الجينية قد تعطل مواقع تحكم حاسمة، وتصميم تجارب أكثر استهدافًا. رغم أن العمل الحالي يستخدم تسلسلات معشّشة كسلبيات اصطناعية ويركز فقط على حروف الـDNA، يخطط المؤلفون لإضافة معلومات هيكلية عن شكل الـDNA واستكشاف تسلسلات خلفية أكثر واقعية. مع تحسّن هذه النماذج، قد تصبح أدوات قوية لفهم كيف تسهم التغيّرات في الـDNA غير المشفر في التطور والتطور والمرض.
الاستشهاد: Dutta, P., Ghosh, N. & Santoni, D. A DNABERT based deep learning framework for predicting transcription factor binding sites. Sci Rep 16, 7018 (2026). https://doi.org/10.1038/s41598-026-37483-1
الكلمات المفتاحية: مواقع ارتباط عوامل النسخ, التعلم العميق, DNABERT, تنظيم الجينات, علم الجينوم