Clear Sky Science · ar
rhinotypeR يمكّن من تعيين الأنماط الجينية للرينوفيروس بصورة قابلة للتكرار من تسلسلات VP4/2
لماذا لا تزال فيروسات البرد الصغيرة مهمة
معظمنا ينظر إلى نزلات البرد على أنها إزعاج أكثر منها تهديدًا خطيرًا. ومع ذلك، فإن الفيروسات المسببة للعديد من حالات البرد — فيروسات الأنف البشرية — مرتبطة أيضًا بعدوى رئوية شديدة ونوبات الربو وتفاقم أمراض الرئة المزمنة. لمتابعة كيف تتطور هذه الفيروسات وتنتشر، يحتاج العلماء إلى تصنيفها إلى "أنماط" جينية دقيقة، مثل إعطاء رموز شريطية للمنتجات. تقدم هذه المقالة rhinotypeR، حزمة برامج مجانية ومفتوحة المصدر تجعل هذه الوسم الجيني أدق وأكثر اتساقًا وأسهل في التكرار، مما يساعد فرق الصحة العامة على متابعة عائلة فيروسات الجهاز التنفسي هذه التي غالبًا ما تُهمل.
التنوع الخفي في نزلات البرد الشائعة
تنتشر فيروسات الأنف البشرية بشكل كبير، وتظهر في ما يصل إلى 60% من العينات المأخوذة من أشخاص يعانون من مرض تنفسي مفاجئ. وهي ليست فيروسًا واحدًا؛ بل تنقسم إلى ثلاث مجموعات رئيسية تُسمى A وB وC، وعلى الأقل 169 نمطًا جينيًا معترفًا به. تختلف الأنماط في سلوكها: فبعضها يرتبط في كثير من الأحيان بعدوى شديدة عند الأطفال ونوبات الربو، في حين أن أنماطًا أخرى تُرى أقل تكرارًا في الأمراض الشديدة. وبما أن هذه الأنماط تتطور بشكل مستقل وتحمل ميزات سطحية مميزة، يحتاج العلماء إلى طرق موثوقة لتمييزها إذا أرادوا تتبع كيفية انتشار التفشيات عبر المدارس والمنازل والمجتمعات.
من أدوات مشتّتة إلى مسار واضح واحد
حتى الآن، كان تعيين نمط رينوفيروس من رمزه الجيني عملًا مرقعًا. عادة ما يركز الباحثون على مقطع قصير من جينوم الفيروس يُسمى منطقة VP4/2، ويقارنونه بسلالات مرجعية معروفة، ويقيسون مدى اختلاف التسلسلات، ثم يطبقون قيم قطع لتحديد أي نمط ينتمي كل عينة إليه. لكن هذه الخطوات كانت تُجرى بمزيج من برامج مختلفة وتحرير يدوي وحكم شخصي. وهذا جعل من الصعب مقارنة الدراسات أو تكرارها، حتى عند استخدام بيانات مماثلة. تم إنشاء rhinotypeR خصيصًا لتحويل هذه العملية متعددة الخطوات والعرضة للأخطاء إلى سير عمل واحد مكتوب يمكن لأي شخص تشغيله ومشاركته.
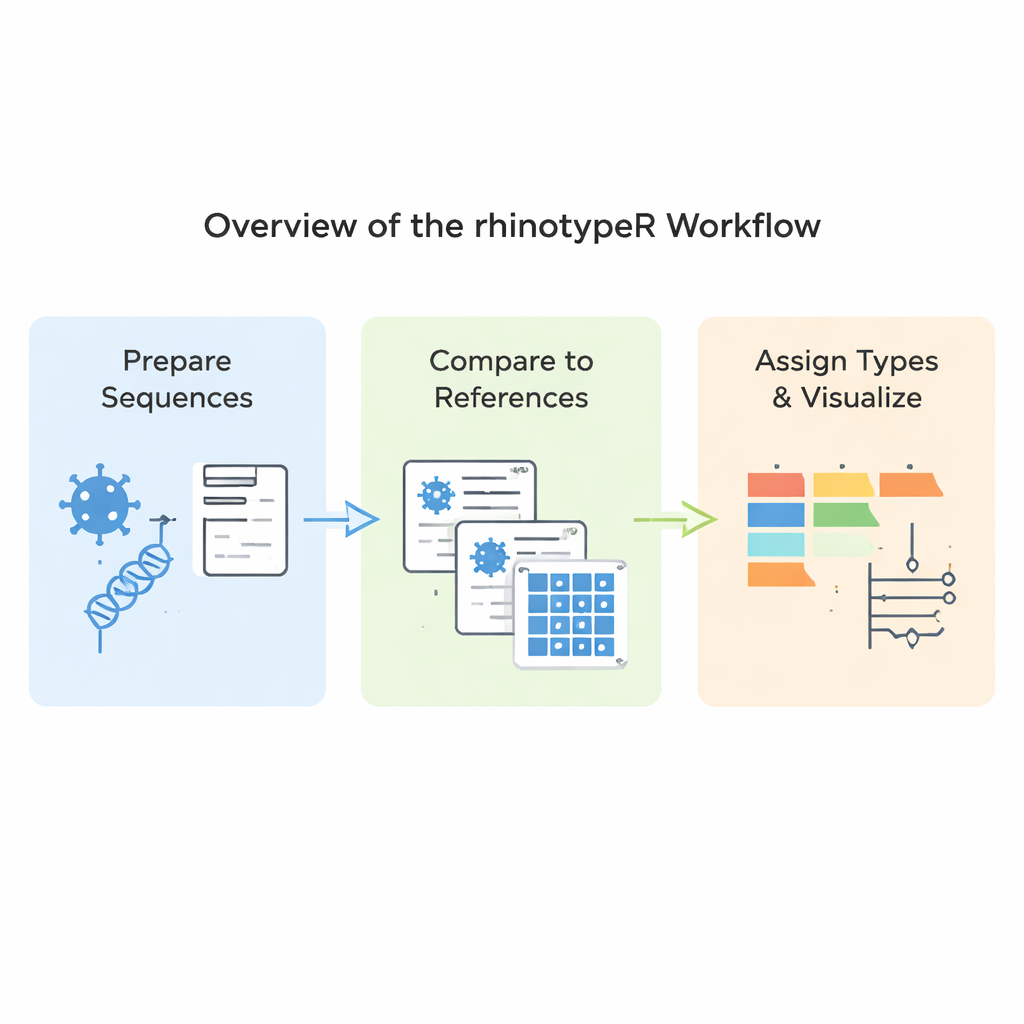
ماذا يفعل البرنامج الجديد فعليًا
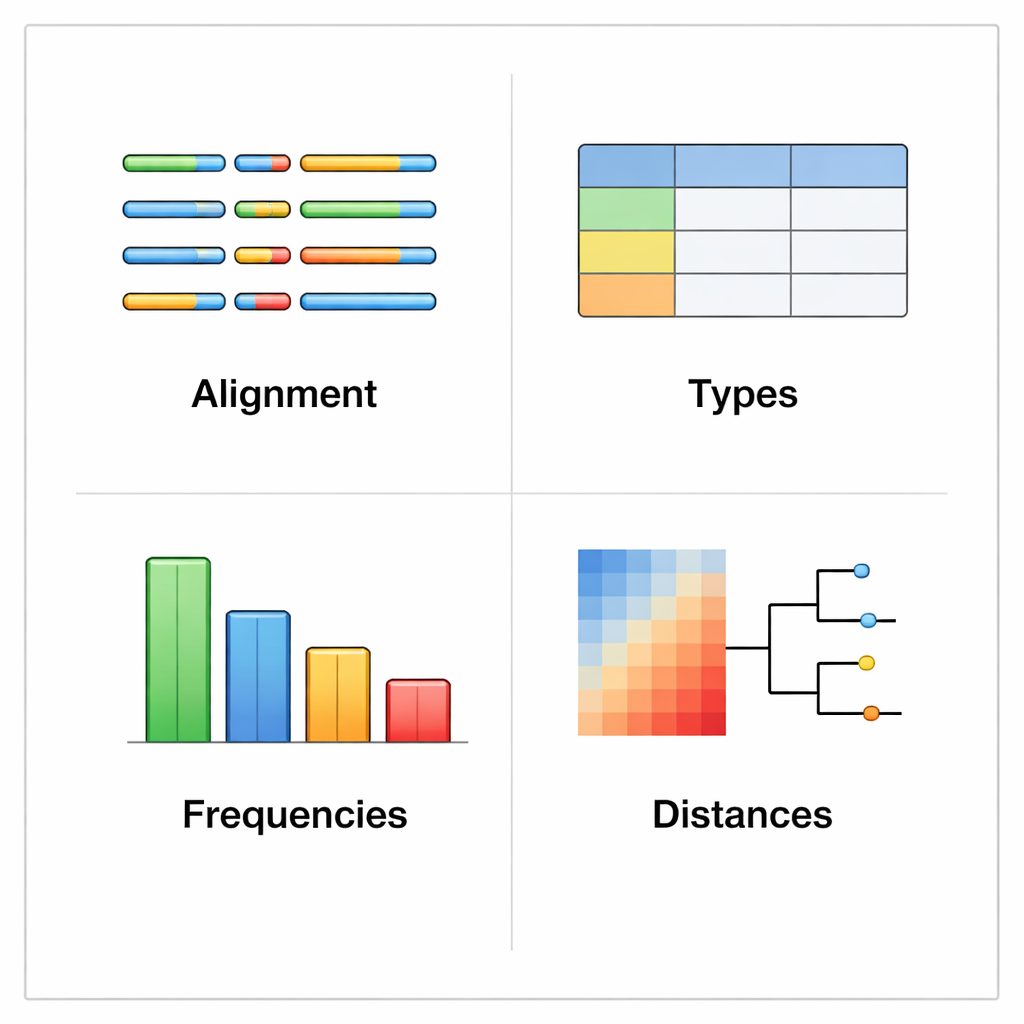
يعمل rhinotypeR داخل بيئة R وBioconductor واسعة الانتشار لتحليل البيانات. يستقبل مجموعة من تسلسلات VP4/2 للرينوفيروس ويمررها بثلاث مراحل رئيسية: تحضير ومحاذاة التسلسلات، حساب مدى تباعد كل تسلسل عن مجموعة مرجعية منظمة من الأنماط، ثم تعيين كل عينة إلى أقرب نمط معروف أو وسمها كـ "غير معين" إذا كانت مختلفة جدًا. يمكن للأداة نفسها إنتاج مخارج مرئية، بما في ذلك خرائط ملونة للاختلافات الجينية، وأشجار عائلية بسيطة، ورسوم بيانية تُظهر مدى شيوع كل نمط في مجموعة بيانات. يمكن للمستخدمين محاذاة بياناتهم عبر برامج خارجية إذا فضلوا ذلك، أو السماح لـ rhinotypeR بإدارة العملية بأكملها داخل R لتحقيق أقصى قدر من القابلية للتكرار.
وضع الأداة قيد الاختبار
للتحقق من أن rhinotypeR يعطي نتائج موثوقة، قارن المؤلفون قياسات المسافة الخاصة به مع تلك من برنامجين راسخين، ape وMEGA X، باستخدام نفس ملفات الإدخال والنماذج. كانت النتائج متطابقة تقريبًا؛ وأي فروق طفيفة عائدة إلى تقريب الأرقام في الحوسبة وليس إلى اختلافات منهجية فعلية. ثم شغّل الفريق rhinotypeR على مجموعة كبيرة تضم أكثر من 2300 تسلسل رينوفيروس من دراسات سابقة متعددة، مغطية أكثر من 90% من الأنماط المعروفة. في حوالي أربع حالات من كل خمس، اتفقت الأداة الجديدة تمامًا مع التسميات النمطية السابقة. حدثت معظم الخلافات عند نقاط القطع المتفق عليها مسبقًا التي تفصل بين نمط وآخر، وهو موضع التوقع لقرارات حدودية. ومن المهم أن العينات التي لم تُعين بثقة إلى نمط معروف لم تُظهر علامات كونها ذات جودة رديئة أو أن مستوى الفيروس فيها منخفض، مما يشير إلى أنها قد تعكس تنوعًا فيروسيًا حقيقيًا.
لماذا هذا مهم للصحة العامة
لغير المتخصصين، الرسالة الأساسية أن rhinotypeR لا يعيد اختراع طريقة تصنيف فيروسات البرد؛ بل يجعل هذه العملية أوضح وأكثر شفافية وأسهل في التكرار. من خلال حزم المحاذاة وحسابات المسافة وتعيين الأنماط في حزمة مفتوحة المصدر واحدة — إلى جانب ملخصات بصرية واضحة — يساعد الباحثين وبرامج المراقبة على معالجة آلاف العينات بطريقة متسقة. تحسّن هذه الاتساق قدرتنا على مقارنة الدراسات من أماكن وأزمنة مختلفة، واكتشاف سلالات فيروسية غير عادية أو ناشئة مبكرًا، وربط الأنماط الجينية باتجاهات المرض في العالم الحقيقي. على المدى الطويل، تعمل أدوات مثل rhinotypeR على تعزيز المراقبة الروتينية لنزلات البرد التي تبدو عادية ولكنها قد تسبب مرضًا شديدًا لدى كثير من الناس.
الاستشهاد: Luka, M.M., Nanjala, R., Rashed, W.M. et al. rhinotypeR enables reproducible rhinovirus genotype assignment from VP4/2 sequences. Sci Rep 16, 6149 (2026). https://doi.org/10.1038/s41598-026-37050-8
الكلمات المفتاحية: تصنيف رينوفيروس جينيًا, المراقبة الجزيئية, تسلسل VP4/2, أدوات المعلوماتية الحيوية, فيروسات الجهاز التنفسي