Clear Sky Science · ar
المسح الآلي لتقدّم شوكات تكرار الحمض النووي في خلايا الإنسان باستخدام ForkML
لماذا يهم تتبّع سرعة نسخ الحمض النووي
في كل مرة تنقسم فيها خلية بشرية، يتعين عليها نسخ أكثر من ثلاثة مليارات حرف من الحمض النووي بسرعة ودقة. إذا تباطأ هذا النسخ أو توقّف، فقد يتعرّض الجينوم للضرر ويساهم ذلك في السرطان واضطرابات النمو. ومع ذلك، حتى الآن، كان العلماء يفتقرون إلى طريقة بسيطة لرؤية السرعة التي تتحرّك بها «آلات النسخ» الفردية على مقاطع محددة من الحمض النووي البشري. تعرض هذه المقالة ForkML، تقنية جديدة تستخدم تسلسل الحمض النووي بنانو بور والتعلّم الآلي لأتمتة هذه المهمة بمقياس غير مسبوق.
مراقبة آلات النسخ داخل الخلية بصورة غير مباشرة
يُضاعَف الحمض النووي بواسطة آليات جزيئية دقيقة تُدعى شوكات التكرار التي تتحرك على الحلزون المزدوج لصياغة سلاسل جديدة. تمكّن ForkML الباحثين من مراقبة هذه الشوكات بصورة غير مباشرة عن طريق إضافة وسم كيميائي غير ضار، BrdU، إلى الحمض النووي المُصاغ حديثًا في نبضتين قصيرتين مفصولتين بزمن ثابت. وبما أن جهازات تسلسل النانو بور تكشف BrdU على جزيئات DNA مفردة، يرى العلماء شريطين موسمين على كل شريط DNA حيث مرت الشوكة أثناء النبضتين. بقياس المسافة بين الشريطين وقسمتها على الفاصل الزمني المعروف، يمكنهم حساب سرعة كل شوكة في تلك المنطقة من الجينوم. 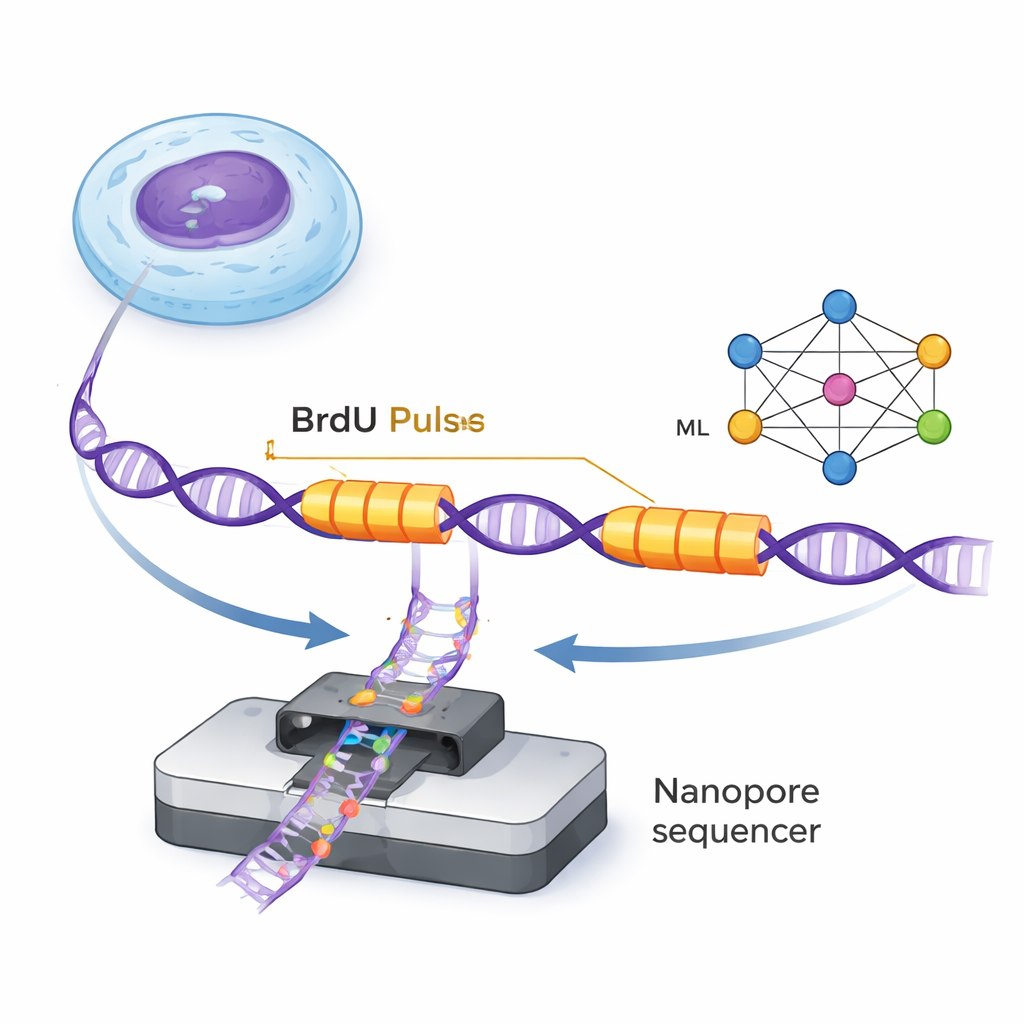
تعليم الحاسوب قراءة الآثار الكيميائية
في أعمال سابقة على الخميرة، كان المؤلفون قادرين على تمييز آثار BrdU باستخدام قواعد بسيطة، لكن في خلايا الإنسان الإشارات أضعف وأكثر تعقيدًا. لا يزال الخبراء البشر يتعرفون على النمط المميّز — ارتفاع حاد في BrdU مع بداية النبضة، يليه تراجع لطيف عند غسله — لكن فحص ملايين قطع DNA بالعين مستحيل. تعالج ForkML هذه المشكلة بتدريب شبكة عصبية، شكل من أشكال التعلّم الآلي، على آلاف الأمثلة المشروحة يدويًا. يتعلّم النموذج تصنيف كل مقطع من الحمض النووي كخلفية أو شوكة تتحرك لليمين أو لليسار، وتحديد بداية كل نبضة BrdU بدقة عالية. وهذا يتيح رسم خرائط آليًا لآلاف سرعات الشوك الفردية من تشغيل تسلسلي واحد.
قياس الإجهاد والاختلافات عبر الجينوم
باستخدام ForkML على خط خلايا سرطان القولون البشري، حصل الفريق على أكثر من 2000 قياس لسرعة الشوكة لكل تجربة ووجد أن الشوكة النموذجية تتحرك بنحو 1.2 كيلوباز في الدقيقة، متوافقًا مع طرق سابقة أقل إنتاجية. عندما عالجوا الخلايا بأدوية معروفة بتباطؤ تكرار الحمض النووي، رصدت ForkML هذا التباطؤ بوضوح، مما يثبت قدرتها على قياس إجهاد التكرار بحساسية. ولأن كل شوكة تُرجع إلى موضعها في الجينوم المرجعي، تمكن المؤلفون من ربط السرعة بميزات أخرى، مثل توقيت تكرار المنطقة خلال دورة الخلية، ومدى تكثيف الحمض النووي فيها، ومدى نشاط تحويلها إلى RNA. 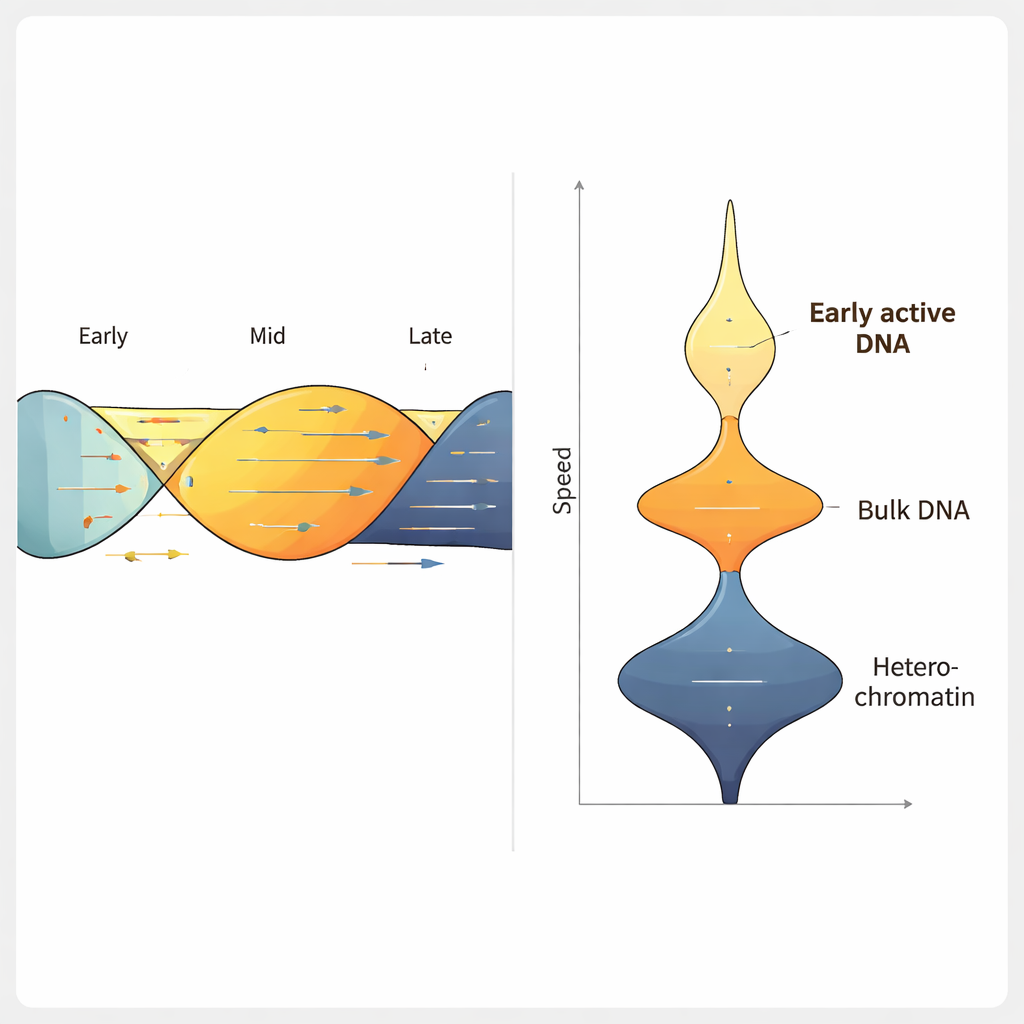
الكشف عن أماكن بدء النسخ وكيف تختلف السلاسِل
بعيدًا عن السرعة، تحدد ForkML أيضًا أين يبدأ وينتهي تكرار الحمض النووي من خلال رصد نقاط تباعد أو تقارب الشوكات على نفس الجزيء. من خلال رسم خرائط أكثر من 20,000 موقع بدء، يؤكد المؤلفون أن خلايا الإنسان تستخدم استراتيجية مختلطة: يبدأ بعض النسخ في مناطق بدء محددة جيدًا، لكن معظم بدايات النسخ موزعة عبر الجينوم. بدمج اتجاه الشوكة مع أي سلسلة DNA قرأها جهاز التتابع، يمكن لـ ForkML أيضًا تمييز معدلات التخليق على الخيط الرائد والخيط المتخلف، وهو ما تعجز عنه تقنيات الألياف التقليدية. اختبارات عبر ستة خطوط خلوية بشرية مختلفة — طبيعية وسرطانية — أظهرت أن نفس شروط وسم BrdU البسيطة تعمل على نطاق واسع وتنتج تقديرات سرعة متينة في كل حالة.
ترقية رقمية لتقنية كلاسيكية
لغير المتخصصين، يمكن اعتبار ForkML نسخة حديثة ورقمية من اختبار ألياف الحمض النووي الكلاسيكي: يستخدم مخطط وسم مشابهًا، لكنه يستبدل المجهر اليدوي بتسلسل قراءات طويلة والتعلّم الآلي. يقدم ذلك إنتاجية أعلى بكثير، وتحديدًا مباشرًا لموقع كل قياس على الجينوم، ومعلومات أكثر تفصيلاً عن أين وبأي سرعة يُنسَخ الحمض النووي. وبما أن البروتوكول بسيط ومتوافق مع أجهزة النانو بور الحالية وقابل للتكيف مع كائنات أخرى، فإن ForkML مرشح لأن يصبح أداة معيارية لدراسة تكرار الحمض النووي. عمليًا، يوفر للباحثين وسيلة قوية لربط سرعة نسخ الحمض النووي المحلية — سواء كانت طبيعية أو متأثرة بالإجهاد — بنشاط الجينات وحالة الكروماتين والتغيرات المرتبطة بالأمراض في الجينوم.
الاستشهاد: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
الكلمات المفتاحية: تكرار الحمض النووي, سرعة شوكة التكرار, تسلسل النانو بور, وسم BrdU, التعلّم الآلي في علم الجينوم