Clear Sky Science · ar
تقييم تقنيات أطلس ATAC-seq على مستوى خلية مفردة باستخدام نمذجة من التسلسل إلى الوظيفة
قراءة كتيب التعليمات داخل الخلية
كل خلية في جسمك تقرأ نفس الـDNA، ومع ذلك تتصرف خلايا الدماغ والعضلات والمناعة بشكل مختلف تمامًا. تتناول هذه الورقة لغزًا جوهريًا وراء هذا التنوع: كيف تعمل مقاطع قصيرة من الـDNA تُسمى المحفِّزات كمفاتيح لتشغيل أو إيقاف الجينات في أنواع خلوية معينة. يبيّن المؤلفون أن تقنيات مخبرية جديدة وأرخص يمكنها توليد مجموعات بيانات ضخمة لازمة لتدريب نماذج التعلم العميق الحديثة التي تقرأ تسلسل الـDNA وتتنبأ بأي المحفِّزات نشطة في أي خلايا، مما يقربنا من فك "قواعد" التنظيم في الجينوم.
رسم خرائط الـDNA المفتوح داخل الخلايا المفردة
عادةً ما تقع المحفِّزات في مقاطع من الـDNA تكون أكثر انفتاحًا وسهلة الوصول، مما يسهل ارتباط بروتينات التنظيم بها. تقنية تُسمى ATAC‑seq على مستوى الخلية الواحدة تقيس أجزاء الجينوم المفتوحة في آلاف إلى مئات الآلاف من الخلايا الفردية دفعة واحدة، مكوّنة "أطلسًا" للـDNA المتاح عبر أنواع خلوية متعددة. هذه الأطلسات تشكّل وقودًا مثالياً لنماذج التعلم العميق التي تتلقى تسلسل الـDNA الخام كمدخل وتتعلم التنبؤ بمدى نشاط كل منطقة صغيرة كمحفِّز في كل نوع خلوي. وحتى الآن، اعتمدت أغلب هذه الأطلسات على أجهزة تجارية مكلفة، مما يثير السؤال عما إذا كانت طرق منخفضة التكلفة ومفتوحة المصدر قادرة على تزويد النماذج ببيانات ذات قيمة مماثلة.
بديل مفتوح المصدر للمنصات التجارية
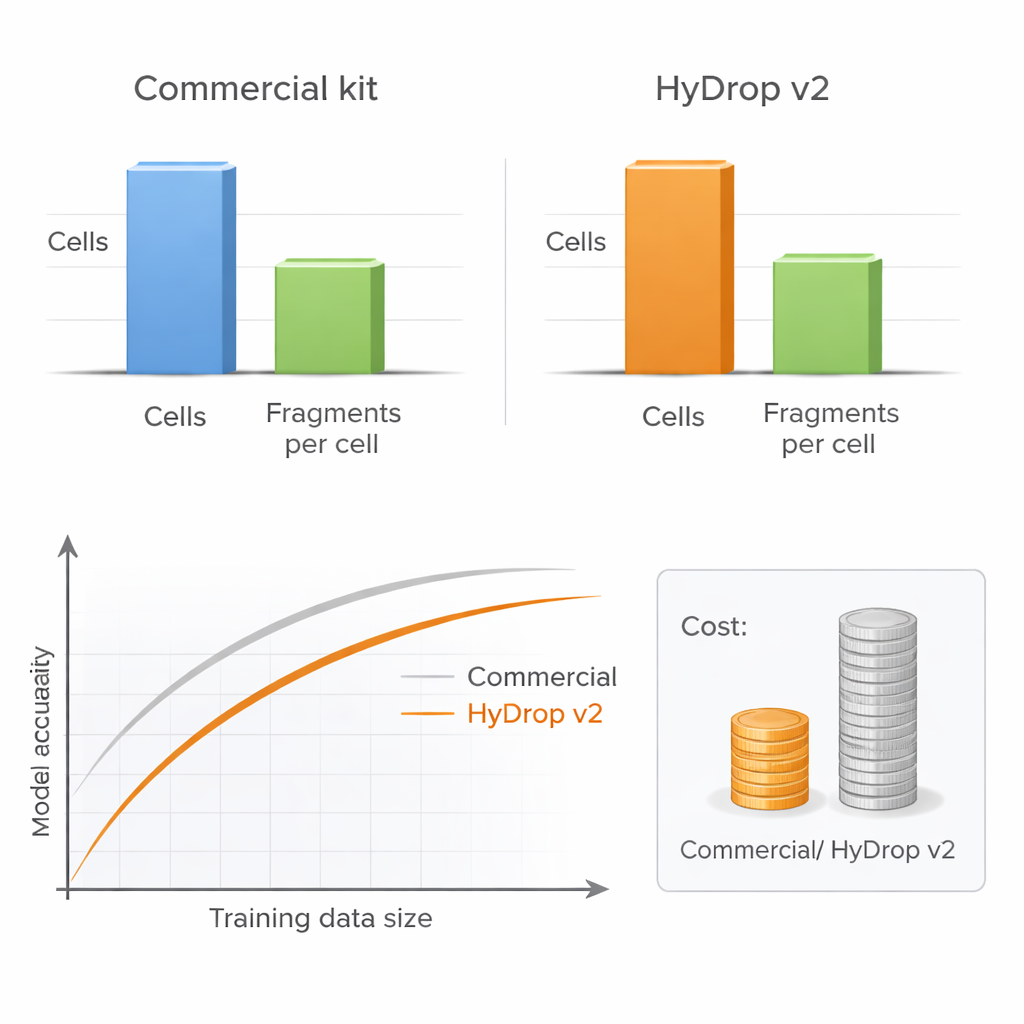
يقدّم المؤلفون HyDrop v2، طريقة محسّنة تعتمد على قطرات الميكروجيوب (droplet) لـATAC‑seq على مستوى الخلية الواحدة تستخدم خرز هيدروجيلية مخصصة لوضع شيفرات تعريف لكل خلية. قارنوا أداء HyDrop v2 مع مجموعة تجارية مستخدمة على نطاق واسع ببناء أطلسات كبيرة من نظامين مختلفين تمامًا: قشرة المخ الحركية لذكر بالغ من الفأر وأجنّة ذبابة الفاكهة في مراحل متأخرة. تولّد HyDrop v2 بيانات بجودة قابلة للمقارنة—تستعيد نفس الأنواع الخلوية الرئيسية ومجموعات متشابهة جدًا من مناطق الـDNA المتاحة—فيما تكلف نحو أربعة عشر مرة أقل لكل عينة دماغ فأر. والأهم أن بيانات تجارب HyDrop v2 تندمج بسلاسة مع البيانات التجارية، ما يمكّن الباحثين من خلط المنصات عند بناء أطلسات كبيرة جدًا.
تدريب نماذج التعلم العميق لقراءة منطق المحفِّزات
لاختبار ما إذا كانت البيانات الأرخص جيدة بما يكفي للنمذجة المتقدمة، درّب الفريق نماذج تعلم عميق من النوع "من التسلسل إلى الوظيفة" إما على أطلسات تجارية أو على أطلسات HyDrop v2. تتعلم هذه النماذج مباشرة من تسلسل الـDNA للتنبؤ بمدى توافر كل منطقة في كل نوع خلوي، ويمكنها إبراز أنماط تسلسلية قصيرة يحتمل أن تمثل مواقع ارتباط لبروتينات تنظيمية محددة. في قشرة الفأر، تساوت نماذج مدرَّبة على بيانات HyDrop v2 مع نماذج البيانات التجارية من حيث الدقة العامة وقدرتها على استرجاع "مفاتيح" المحفِّز المعروفة التي تم التحقق منها سابقًا في حيوانات حية. في جنين الذبابة، دعمت كلتا المنصتين نماذج تستطيع التكبير إلى مناطق بطول 2000 زوج قواعد وتحديد المقاطع الأساسية بنحو ~500 زوج قواعد التي تحرّك فعليًا النشاط المحفِّز النسيجي، مثل المناطق التي تتحكم في التعبير الجيني للخلايا العصبية الأولية أو خلايا العضلات.
عدد خلايا أكبر يفوق عمق تسلسل أعلى
سؤال عملي أساسي لأي مختبر هو ما إذا كان من الأفضل تسلسل كل خلية بعمق عالٍ أم تحليل عدد أكبر من الخلايا بعمق أقل. من خلال تغيير منهجي في عدد الخلايا وعدد شظايا الـDNA لكل خلية، يوضح المؤلفون أن أداء النماذج لا يهبط كثيرًا عندما يُخفض عمق التسلسل إلى مستوى معتدل، شريطة شمول عدد كافٍ من الخلايا. بالمقابل، يؤدي تقليص عدد الخلايا إلى إضعاف دقة النموذج بوضوح، لا سيما عند قياس الأداء عبر العديد من أنواع الخلايا دفعة واحدة. وبما أن HyDrop v2 أرخص بكثير لكل خلية، يمكن للباحثين إضافة عشرات الآلاف من الخلايا الإضافية بسهولة، مسترجعين أو متجاوزين أداء النماذج المعتمدة على منصات تجارية بجزء بسيط من التكلفة.
رؤية آثار البروتينات على الـDNA
تفحص الدراسة أيضًا ما إذا كانت المنصات المخبرية المختلفة تُدخل تحيّزات دقيقة في كيفية قطع إنزيم ATAC‑seq للـDNA، وهو ما قد يضلل النماذج التي تحاول استنتاج مواقع البروتينات على الجينوم. باستخدام أداة شبكة عصبية منفصلة تصحّح تفضيلات الإنزيم، يبيّن المؤلفون أن HyDrop v2 والمجموعات التجارية تنتجان أنماط نشاط إنزيمي متماثلة تقريبًا في خلايا الفأر والذبابة. بعد التصحيح، تكشف كلتا مجموعتي البيانات عن "بصمات" دقيقة حيث تحمي البروتينات التنظيمية والنيوكليوزومات الـDNA من القطع، وتتطابق هذه البصمات مع الأنماط التسلسلية التي أبرزتها نماذج التسلسل‑إلى‑الوظيفة. هذا الاتساق يشير إلى أن المنصات مفتوحة المصدر والتجارية مناسبة بالمثل للدراسات التفصيلية لكيفية تفاعل البروتينات مع الـDNA.
لماذا يهم هذا لفك شيفرة الجينوم
للغير مختصين، الخلاصة هي أننا بات بإمكاننا الآن بناء خرائط ضخمة وميسورة التكلفة لكيفية استخدام الـDNA في الخلايا الفردية، وتدريب نماذج تعلم عميق قوية على تلك الخرائط دون الاعتماد فقط على أجهزة مملوكة مكلفة. تقدّم HyDrop v2 بيانات تدعم التنبؤ بالمحفِّزات، وتفسير أنماط التسلسل، وبصمات ارتباط البروتينات على قدم المساواة مع أفضل الطرق التجارية، بشرط تحليل عدد كافٍ من الخلايا. يفتح هذا الباب لبناء أطلسات على مستوى الكائن الحي لعناصر التنظيم في الصحة والمرض، مع تسريع جهود قراءة تعليمات الجينوم وتصميم مفاتيح جينية جديدة دقيقة الاستهداف للأبحاث والعلاجات المستقبلية.
الاستشهاد: Dickmänken, H., Wojno, M., Mahieu, L. et al. Evaluating single-cell ATAC-seq atlasing technologies using sequence-to-function modeling. Nat Commun 17, 1951 (2026). https://doi.org/10.1038/s41467-026-68742-4
الكلمات المفتاحية: ATAC-seq على مستوى الخلية الواحدة, المُحفِزات (Enhancers), نماذج التعلم العميق, تنظيم الجينات, علم الجينوم مفتوح المصدر